Анализы крови — простые, неинвазивные и экономически целесообразные — обещают стать следующей важной вехой в диагностике рака. Однако большинство этих тестов, получивших название жидкостной биопсии, в настоящее время недостаточно надежны для широкого использования. Новый многопараметрический подход, разработанный в Научном институте Вейцмана, может привести к анализу крови, который позволит диагностировать рак с беспрецедентной точностью. Это исследование публикуется сегодня в журнале Nature Biotechnology.
«Многие из обычных методов, доступных сегодня в клинике для обнаружения и диагностики рака, являются инвазивными и неприятными», — объясняет доктор Эфрат Шема из отдела иммунологии и регенеративной биологии Вейцмана, который возглавлял исследовательскую группу. Получение образцов биопсии с помощью иглы, эндоскопии или хирургического вмешательства может быть болезненным, а иногда и рискованным, а методы визуализации, такие как МРТ или ПЭТ, требуют дорогостоящего громоздкого оборудования, которое не всегда доступно. Эффективные анализы крови для скрининга или диагностики рака могут стать привлекательной альтернативой.
«Устранение дискомфорта означает, что люди с меньшей вероятностью будут избегать тестирования и с большей вероятностью выявят рак раньше», — говорит Вадим Федюк, который руководил исследованием вместе с сокурсником Ниром Эрезом.
Идея диагностики рака с помощью жидких биопсий возникла из-за того, что кровь содержит свободно плавающие ДНК и белки, выделяемые мертвыми клетками крови у здоровых людей, а у больных раком — и мертвыми опухолевыми клетками. «Некоторые побочные продукты разрушения клеток, в том числе ДНК и белки рака, попадают в кровоток, и мы знаем, как их собирать и анализировать», — говорит Шема.
Ряд анализов крови на рак уже находятся на продвинутой стадии разработки, но большинство из них имеют недостатки, которые могут ограничивать их использование. Когда были разработаны первые такие тесты, они искали генетические признаки рака, то есть мутации, но их может быть трудно определить, потому что мутировавшие сегменты составляют лишь небольшую часть свободно циркулирующей ДНК. Более того, эти мутации не всегда приводят к раку и могут быть и у здоровых людей. Совсем недавно подходы жидкой биопсии стали основываться на эпигенетике или модификациях генома клетки, не связанных с мутациями в ДНК — например, химические метки, которые прикрепляются к молекуле ДНК, изменяя экспрессию генов. Эти подходы также столкнулись с проблемами.
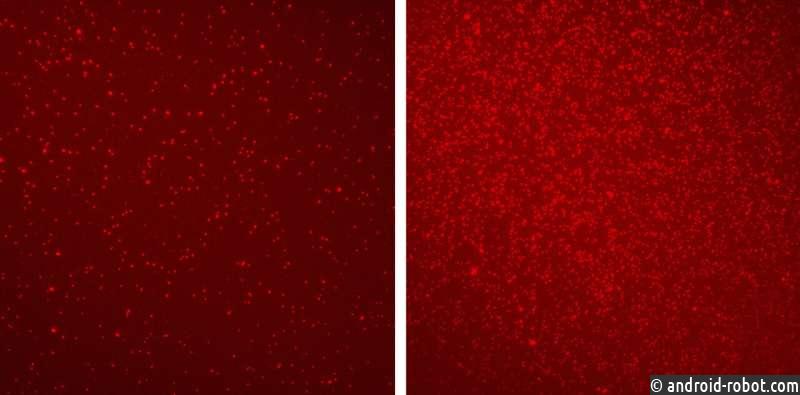
В новом исследовании Шема решил переосмыслить этот эпигенетический анализ, стремясь разработать такой, который будет опираться на небольшой образец крови для оценки нескольких эпигенетических параметров. Она основывалась на методе визуализации отдельных молекул, который она разработала во время своего постдокторского исследования в Гарвардской медицинской школе и Институте Броуда. Этот метод позволяет получить точное эпигенетическое картирование только с очень небольшим количеством исходного материала с использованием флуоресцентного микроскопа. Его можно использовать, например, для просмотра эпигенетических меток на нуклеосомах, фрагментах ДНК, обернутых вокруг белковых «катушек». Они могут попасть в кровоток, как обломки мусора, когда клетки разрушаются, поэтому Шема рассудил, что миллионы нуклеосом, обнаруженных в крови, могут быть проанализированы для обнаружения рака.
Используя метод визуализации одиночных молекул Шемы, Федюк и Эрез вместе с коллегами сравнили нуклеосомы в крови 30 здоровых людей с нуклеосомами 60 пациентов с разными стадиями колоректального рака. Они обнаружили, что нуклеосомы двух групп характеризовались совершенно разными паттернами эпигенетической маркировки. Этот анализ охватил шесть различных эпигенетических модификаций, связанных с раком, а также множество других индикаторов рака, включая сегменты белка из мертвых опухолей, которые невозможно обнаружить с помощью обычных технологий.
Затем в сотрудничестве с профессором Гаем Роном из Института физики Рака при Еврейском университете в Иерусалиме ученые объединили то, что они узнали о молекулярной биологии рака, с алгоритмами искусственного интеллекта , применив машинное обучение к большим наборам данных, полученным из две группы. Анализ проводился не только по всем этим онкомаркерам, но и по комбинациям и взаимосвязям между ними. Чтобы убедиться, что их выводы не ограничиваются колоректальным раком, ученые также применили свою технологию для сравнения нуклеосом крови здоровых добровольцев с нуклеосомами крови 10 пациентов с раком поджелудочной железы.
«Наш алгоритм может определить разницу между группами здоровых и пациентов с рекордным уровнем достоверности для исследований такого типа — с точностью 92%», — говорит Шема. Ученые называют новую технологию EPINUC, что означает «эпигенетика изолированных в плазме нуклеосом».
Если эти результаты будут подтверждены исследованиями с участием большего числа пациентов, эти результаты могут привести к многопараметрическому анализу крови для обнаружения и диагностики рака с использованием менее 1 мл крови. В будущем, из-за уровня детализации, выявленного в анализе, результаты этого анализа крови могут также продвинуть персонализированную медицину, предлагая лучшие методы лечения для каждого отдельного пациента.
Шема резюмирует: «Мы добились успешного доказательства концепции нашего метода, который теперь должен быть подтвержден в клинических испытаниях. В будущем наш многопараметрический подход может служить для диагностики не только различных видов рака, но и других заболеваний, которые оставляют следы. в крови, например, при аутоиммунных заболеваниях или сердечных заболеваниях».